AutoDock Vina
< Podręcznik użytkownika KDM < Oprogramowanie KDM < Oprogramowanie naukowe
| AutoDock Vina | |
|---|---|
| Serwer | Wersja |
| Nova | 1 |
| Kontakt | |
| kdm@wcss.pl | |
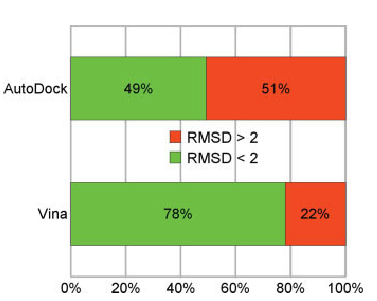
AutoDock Vina - program wykorzystywany do dokowania molekularnego oraz screeningu układów białko-ligand. Implementacja nowych algorytmów optymalizacji, funkcji dopasowania (scoring function) oraz wprowadzenie możliwości zrównoleglenia obliczeń zaowocowało wynikami lepszej jakości uzyskanymi w do 2 rzędów krótszym czasie względem poprzedniej generacji oprogramowania (AutoDock4.x).
Przepływ danych
Na każdym etapie można zastosować alternatywne oprogramowanie.
- Przygotowanie pliku wsadowego w MGLTools (*.PDBQT).
- przygotowanie struktury białka (dodanie wodorów, określenie rozmiaru przestrzeni dopasowania)
- przygotowanie ligandu (określenie wiązań rotacyjnych)
- Przeprowadzenie obliczeń w AutoDock Vina w WCSS.
- AutoDock Vina uruchamiany jest skryptem
sub-autodock-vina
- AutoDock Vina uruchamiany jest skryptem
- Interpretacja wyników w PyMOL.
Licencja
Program udostępniony jest na licencji Apache, z kilkoma zastrzeżeniami co do użytku komercyjnego, niekomercyjnego i prac wywiedzionych (tekst licencji)
W publikacjach, w których do liczenia korzystano z AutoDock Vina, należy cytować artykuł: "O. Trott, A. J. Olson, AutoDock Vina: improving the speed and accuracy of docking with a new scoring function, efficient optimization and multithreading, Journal of Computational Chemistry 31 (2010) 455-461"